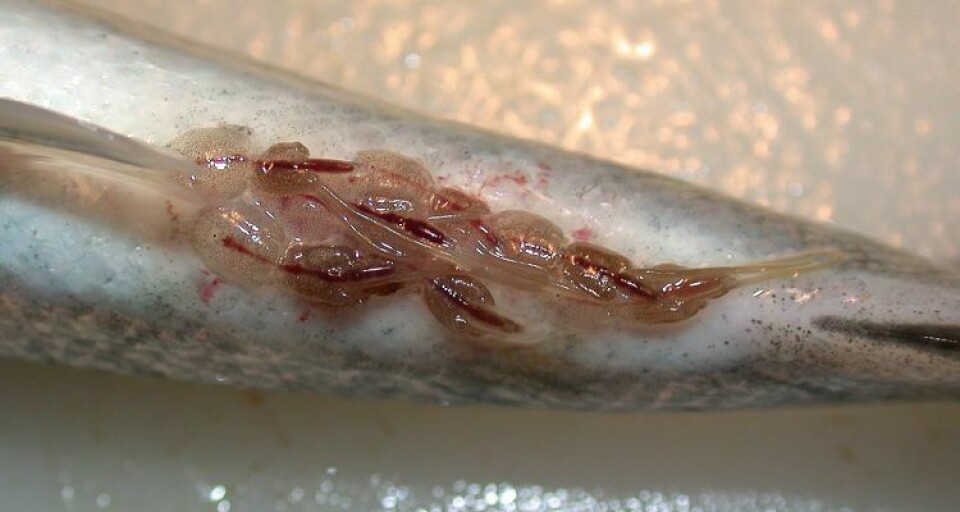
Descubren QTLs que explicarían hasta 13% de resistencia a Caligus
Chile: El reciente estudio científico fue realizado en 2.668 salmones Atlántico de 104 familias de la población de reproductores del centro AquaInnovo, Puerto Montt.
Identificar regiones del genoma asociadas a algún rasgo de interés, o también denominadas QTLs (del Inglés Quantitative Trait Loci), es sumamente difícil.
Sin embargo, científicos de la Universidad de Edinburgo, Reino Unido, Universidad de Chile, Benchmark Genetics Chile y el Núcleo Milenio Invasal, Chile, lograron identificar QTLs que, según los investigadores, explicaría entre el 7% y 13% de la resistencia genética del salmón Atlántico al Caligus.
La investigación fue realizada en 2.668 salmones Atlántico de 104 familias de la población de reproductores del centro AquaInnovo (Hoy parte de Benchmark Genetics), Puerto Montt. Luego de un ensayo de infección experimental con Caligus, los investigadores tomaron muestras de los peces infectados para proceder a realizar una serie de análisis genéticos que los ayudaran a evidenciar una posible resistencia genética al parásito.
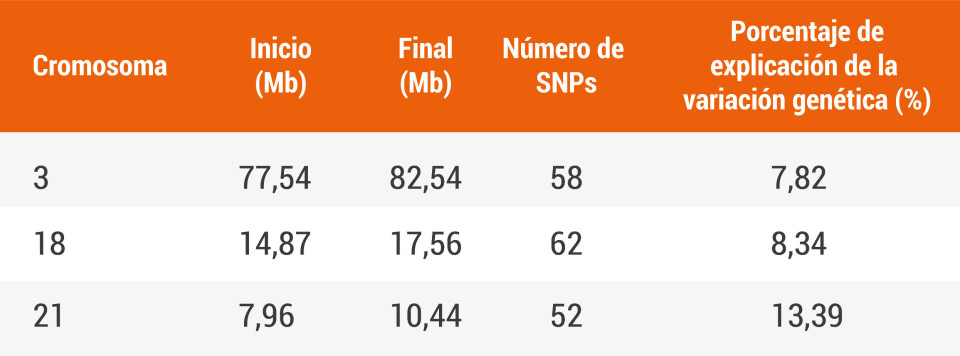
Con estos resultados, lograron evidenciar que, en conjunto, tres QTLs ubicados en tres cromosomas serían los involucrados en los rasgos genéticos que podrían explicar la resistencia a la infección.
“Se detectaron tres QTL que explican entre el 7% y el 13% de la variación genética en la resistencia al piojos de mar (representados como la densidad de piojos) en los cromosomas 3, 18 y 21”, señalaron los autores del estudio.
Además, mediante una caracterización genética, también intentaron decifrar los posibles genes y mutaciones de las regiones donde se ubican los QTLs, lo que dió como resultado una lista de posibles genes causantes subyacentes y mutaciones funcionales candidatas.
Por ejemplo, según lo expuesto por los autores en sus conclusiones, un supuesto codón de parada prematuro dentro de TOB1, una proteína antiproliferativa, parece un candidato plausible para explicar el QTL en el cromosoma 3. Sumado a lo anterior, STK17B, conectado funcionalmente a la proliferación y función de las células T, es un candidato plausible para el QTL en el cromosoma 21.
Así, los expertos concluyeron que “si bien la resistencia del hospedador al piojo de mar es de naturaleza poligénica, los resultados de este estudio resaltan regiones QTL significativas que explican en conjunto entre el 7% y el 13% de la heredabilidad del rasgo. La investigación futura de estos QTL puede permitir un mejor conocimiento de los mecanismos funcionales de la resistencia del hospedador al piojo de mar, y la incorporación de variantes funcionales para mejorar la precisión de la selección genómica”.
Lea el artículo titulado “Discovery and Functional Annotation of Quantitative Trait Loci Affecting Resistance to Sea Lice in Atlantic Salmon” aquí.




















